1 材料与方法
1.1 样本
按照知情同意原则,用FTA采血卡采集200例四川省北川羌族健康无关个体的血样,其中男性171例,女性29例。
通过Ensembl数据库(
表1 数据库中26个人群的信息
Tab. 1
| 人群 | 缩写 | 样本量/例 | 所属地区 | 人群 | 缩写 | 样本量/例 | 所属地区 |
|---|---|---|---|---|---|---|---|
| 西双版纳傣族 | CDX | 94 | 东亚 | 冈比亚西部人 | GWD | 113 | 非洲 |
| 北京汉族 | CHB | 103 | 东亚 | 肯尼亚卢希亚人 | LWK | 99 | 非洲 |
| 南方汉族 | CHS | 105 | 东亚 | 塞拉利昂曼迪人 | MSL | 85 | 非洲 |
| 东京日本人 | JPT | 104 | 东亚 | 尼日利亚约鲁巴人 | YRI | 108 | 非洲 |
| 越南京族人 | KHV | 99 | 东亚 | 麦德林哥伦比亚人 | CLM | 94 | 美洲 |
| 孟加拉人 | BEB | 86 | 南亚 | 洛杉矶墨西哥人 | MXL | 63 | 美洲 |
| 休斯敦古吉拉特人 | GIH | 103 | 南亚 | 秘鲁利马人 | PEL | 85 | 美洲 |
| 英国泰卢固族人 | ITU | 102 | 南亚 | 波多黎各人 | PUR | 104 | 美洲 |
| 巴基斯坦拉合尔旁遮普人 | PTL | 96 | 南亚 | 犹他州北欧和西欧人 | CEU | 99 | 欧洲 |
| 美国斯里兰卡泰米尔人 | STU | 102 | 南亚 | 芬兰人 | FIN | 99 | 欧洲 |
| 巴巴多斯人 | ACB | 96 | 非洲 | 英国人 | GBR | 91 | 欧洲 |
| 非洲裔美国人 | ASW | 61 | 非洲 | 西班牙伊比利亚人 | IBS | 107 | 欧洲 |
| 尼日利亚埃桑人 | ESN | 99 | 非洲 | 意大利托斯卡纳人 | TSI | 107 | 欧洲 |
本研究已获得川北医学院伦理委员会批准,审批文号为[2021]14号。
1.2 PCR扩增
根据AGCU InDel 60荧光检测试剂盒说明书,采用直接扩增法(免提取)对血样进行PCR扩增。扩增体系为10 μL,其中Reaction Mix 4 μL、InDel 60 Primers 2 μL、热启动U-Taq酶0.4 μL、去离子水3.6 μL,模板DNA为直径1.2 mm的血斑1片。采用9700型PCR仪(美国Applied Biosystems公司)进行扩增,扩增条件:95 ℃预变性5 min;94 ℃ 30 s,60 ℃ 60 s,62 ℃ 60 s,25个循环;72 ℃延伸10 min,4 ℃保存备用。
1.3 毛细管电泳和数据分析
采用3500基因分析仪(美国Applied Biosystems公司)进行毛细管电泳。取1 μL PCR产物、10 μL去离子甲酰胺和0.3 μL内标AGCU Marker SIZ-500混匀,95 ℃变性3 min后,立即冰浴3 min。用GeneMapper®ID-X 1.4软件(美国Thermo Fisher Scientific公司)进行分型。InDel位点中的插入(insertion)等位基因和缺失(deletion)等位基因分别命名为I和D,Amelogenin位点的两个等位基因分别为X和Y。
1.4 质量控制
每批样本的检测均采用去离子水和标准品9948分别作为扩增的阴性对照和阳性对照。
1.5 统计分析
采用Modified-Powerstats标准版软件计算获得57个A-InDel位点的等位基因频率(Fins和Fdel)、DP、PIC、CDP。采用Cervus 3.0.7软件(
2 结 果
2.1 等位基因分型结果
200例北川羌族无关个体的血样中,57个A-InDel、2个Y-InDel和Amelogenin位点均得到有效扩增,扩增产物片段均在80~230 bp,InDel位点信息见表2。男性样本的Y-InDel位点检测到1个等位基因,Amelogenin位点检测结果为XY;女性样本的Y-InDel位点检测结果为阴性,Amelogenin位点检测结果为X。
表2 北川羌族人群59个A-InDel位点的基本信息
Tab. 2
| 位点 | 染色体定位 | InDel序列 | 位点 | 染色体定位 | InDel序列 |
|---|---|---|---|---|---|
| rs34421865 | 15q21.1 | CTCT | rs59841142 | 1q24.1 | CTAA |
| rs3076465 | 11q22.3 | ATAA | rs145010051 | 16q24.3 | GGA |
| rs34287950 | 10q25.2 | TTT | rs66477007 | 3q13.2 | TCTT |
| rs151335218 | 7q31.1 | AAGT | rs142221201 | 7q33 | AAAG |
| rs5787309 | 10q24.2 | TTATT | rs67426579 | 7q11.23 | GTG |
| rs67405073 | 9q33.3 | TGA | rs145941537 | 12q14.3 | AATT |
| rs60867863 | 6p25.1 | ATTA | rs67365630 | 8q24.3 | ACT |
| rs71852971 | 1p22.1 | ACTC | rs3064355 | 4q28.3 | AAG |
| rs769299 | 11q14.1 | GATA | rs60564093 | 8q12.3 | TCA |
| rs10590825 | 3q23 | CCT | rs34076006 | 2q23.1 | AAG |
| rs79225518 | 6q26 | AAG | rs3834231 | 4p16.1 | CCTA |
| rs140683187 | 10p13 | AAC | rs61490765 | 14q32.12 | TTAAT |
| rs57981446 | 8q23.3 | AGGAG | rs72085595 | 19q13.11 | TGTC |
| rs145191158 | 3p14.3 | TTTG | rs76158822 | 9p21.3 | TTAAG |
| rs10626599 | 15q26.2 | TGTGC | rs67487831 | 1q43 | TCAA |
| rs112879447 | 6p21.33 | TATAAC | rs66595817 | 5q22.3 | CTTTC |
| rs10607699 | 1p31.3 | CCT | rs35065898 | 13q33.1 | ACTT |
| rs35309403 | 4q26 | ACTG | rs76041101 | Yq11.221 | AGT |
| rs145577149 | 4p12 | AAAT | rs199815934 | Yq11.221 | CTTCT |
| rs113011930 | 2p16.1 | TTCT | rs34529638 | 19q13.2 | CCT |
| rs35453727 | 13q12.2 | AGA | rs67264216 | 12q24.33 | TGTCG |
| rs5897566 | 9p13.3 | TAAC | rs3067397 | 1p31.3 | AGATA |
| rs1160980 | 5q23.3 | GAT | rs11277697 | 2p25.3 | TTAGG |
| rs77206391 | 18q12.1 | ACAA | rs72031009 | 17q22 | TAGAG |
| rs35464887 | 9p21.3 | TTTA | rs33971783 | 19p13.12 | TGTT |
| rs67100350 | 11p15.1 | TAGT | rs146875868 | 2q37.2 | TCTT |
| rs538690481 | 21q22.11 | TCTGAA | rs34419736 | 15q13.1 | AAG |
| rs67939200 | 12q12 | TCA | rs77635204 | 15q14 | AGAA |
| rs66739142 | 15q23 | TCTTT | rs561160795 | 14q23.3 | TGG |
| rs3217112 | 7p14.2 | TAATA |
2.2 Hardy-Weinberg平衡检验
经Hardy-Weinberg平衡检验,57个A-InDel位点中,除rs5787309、rs10590825、rs1160980、rs33971783和rs561160795外,其余52个位点均符合Hardy-Weinberg平衡(P>0.05)。采用Bonferroni法进行校正,57个A-InDel位点的P值均大于0.000 88(0.05/57),表明所有位点均符合Hardy-Weinberg平衡。
2.3 连锁不平衡检验
57个A-InDel位点两两之间共进行了1 596次连锁不平衡检验,其中87次比较结果的P值为0.000 947~0.049 932,且该87对两两比较的位点均位于不同的染色体上。经过Bonferroni法校正,各位点间均不存在连锁不平衡现象[P值均大于0.000 031(0.05/1 596)]。
2.4 等位基因频率及群体遗传学参数
57个A-InDel位点的等位基因频率及群体遗传学参数见表3。Fdel值为0.272 5~0.760 0,Fins值为0.240 0~0.727 5;Ho值为0.370 0~0.585 0,He值为0.365 7~0.501 2,PIC值为0.298 3~0.375 0,DP值为0.529 5~0.659 0,PEtrio值为0.234 9~0.281 2,PEduo值为0.066 5~0.125 0。由于57个A-InDel位点间处于连锁平衡状态,故可采用乘积定律计算其CDP和CPE。57个A-InDel位点在北川羌族人群中的CDP值为1-2.974 8×10-24,CPEtrio值为0.999 999 999,CPEduo值为0.999 062 660。
表3 北川羌族人群57个A-InDel位点的等位基因频率及群体遗传学参数
Tab. 3
| 位点 | Fdel | Fins | DP | Ho | He | PIC | PEduo | PEtrio | Fst |
|---|---|---|---|---|---|---|---|---|---|
| rs34421865 | 0.452 5 | 0.547 5 | 0.632 1 | 0.475 0 | 0.496 7 | 0.372 7 | 0.122 8 | 0.279 8 | 0.062 3 |
| rs3076465 | 0.432 5 | 0.567 5 | 0.602 5 | 0.525 0 | 0.492 1 | 0.370 4 | 0.120 5 | 0.278 4 | 0.111 7 |
| rs34287950 | 0.580 0 | 0.420 0 | 0.625 9 | 0.470 0 | 0.488 4 | 0.368 5 | 0.118 7 | 0.277 2 | 0.216 2 |
| rs151335218 | 0.515 0 | 0.485 0 | 0.638 2 | 0.470 0 | 0.500 8 | 0.374 8 | 0.124 8 | 0.281 1 | 0.038 8 |
| rs5787309 | 0.517 5 | 0.482 5 | 0.571 1 | 0.585 0 | 0.500 6 | 0.374 7 | 0.124 7 | 0.281 1 | 0.094 2 |
| rs67405073 | 0.577 5 | 0.422 5 | 0.587 5 | 0.545 0 | 0.489 2 | 0.368 9 | 0.119 1 | 0.277 5 | 0.092 7 |
| rs60867863 | 0.507 5 | 0.492 5 | 0.627 4 | 0.495 0 | 0.501 1 | 0.374 9 | 0.124 9 | 0.281 2 | 0.236 1 |
| rs71852971 | 0.695 0 | 0.305 0 | 0.581 8 | 0.410 0 | 0.425 0 | 0.334 1 | 0.089 9 | 0.256 4 | 0.210 7 |
| rs769299 | 0.385 0 | 0.615 0 | 0.616 2 | 0.460 0 | 0.474 7 | 0.361 4 | 0.112 1 | 0.272 9 | 0.040 0 |
| rs10590825 | 0.497 5 | 0.502 5 | 0.659 0 | 0.405 0 | 0.501 2 | 0.375 0 | 0.125 0 | 0.281 2 | 0.018 1 |
| rs79225518 | 0.540 0 | 0.460 0 | 0.643 1 | 0.450 0 | 0.498 0 | 0.373 4 | 0.123 4 | 0.280 2 | 0.164 1 |
| rs140683187 | 0.635 0 | 0.365 0 | 0.602 2 | 0.470 0 | 0.464 7 | 0.356 1 | 0.107 4 | 0.269 7 | 0.025 7 |
| rs57981446 | 0.520 0 | 0.480 0 | 0.613 6 | 0.520 0 | 0.500 5 | 0.374 6 | 0.124 6 | 0.281 0 | 0.196 4 |
| rs145191158 | 0.512 5 | 0.487 5 | 0.622 2 | 0.505 0 | 0.500 9 | 0.374 8 | 0.124 8 | 0.281 2 | 0.192 4 |
| rs10626599 | 0.570 0 | 0.430 0 | 0.624 6 | 0.480 0 | 0.491 4 | 0.370 1 | 0.120 1 | 0.278 2 | 0.007 8 |
| rs112879447 | 0.512 5 | 0.487 5 | 0.585 9 | 0.565 0 | 0.500 9 | 0.374 8 | 0.124 8 | 0.281 2 | 0.010 7 |
| rs10607699 | 0.320 0 | 0.680 0 | 0.587 9 | 0.430 0 | 0.436 3 | 0.340 5 | 0.094 7 | 0.260 3 | 0.009 9 |
| rs35309403 | 0.385 0 | 0.615 0 | 0.612 2 | 0.470 0 | 0.474 7 | 0.361 4 | 0.112 1 | 0.272 9 | 0.082 0 |
| rs145577149 | 0.622 5 | 0.377 5 | 0.610 7 | 0.465 0 | 0.471 2 | 0.359 5 | 0.110 4 | 0.271 7 | 0.059 6 |
| rs113011930 | 0.485 0 | 0.515 0 | 0.608 2 | 0.530 0 | 0.500 8 | 0.374 8 | 0.124 8 | 0.281 1 | 0.250 3 |
| rs35453727 | 0.562 5 | 0.437 5 | 0.624 4 | 0.485 0 | 0.493 4 | 0.371 1 | 0.121 1 | 0.278 8 | 0.127 8 |
| rs5897566 | 0.325 0 | 0.675 0 | 0.591 4 | 0.430 0 | 0.439 8 | 0.342 5 | 0.096 3 | 0.261 5 | 0.182 2 |
| rs1160980 | 0.587 5 | 0.412 5 | 0.643 7 | 0.405 0 | 0.485 9 | 0.367 2 | 0.117 5 | 0.276 4 | 0.042 8 |
| rs77206391 | 0.502 5 | 0.497 5 | 0.617 2 | 0.515 0 | 0.501 2 | 0.375 0 | 0.125 0 | 0.281 2 | 0.184 5 |
| rs35464887 | 0.560 0 | 0.440 0 | 0.582 4 | 0.560 0 | 0.494 0 | 0.371 4 | 0.121 4 | 0.279 0 | 0.034 7 |
| rs67100350 | 0.395 0 | 0.605 0 | 0.616 6 | 0.470 0 | 0.479 1 | 0.363 7 | 0.114 2 | 0.274 3 | 0.137 9 |
| rs538690481 | 0.635 0 | 0.365 0 | 0.609 8 | 0.450 0 | 0.464 7 | 0.356 1 | 0.107 4 | 0.269 7 | 0.150 5 |
| rs67939200 | 0.565 0 | 0.435 0 | 0.644 2 | 0.430 0 | 0.492 8 | 0.370 7 | 0.120 8 | 0.278 6 | 0.056 3 |
| rs66739142 | 0.460 0 | 0.540 0 | 0.593 1 | 0.550 0 | 0.498 0 | 0.373 4 | 0.123 4 | 0.280 2 | 0.117 7 |
| rs3217112 | 0.417 5 | 0.582 5 | 0.623 0 | 0.475 0 | 0.487 6 | 0.368 1 | 0.118 3 | 0.277 0 | 0.065 3 |
| rs59841142 | 0.492 5 | 0.507 5 | 0.636 5 | 0.475 0 | 0.501 1 | 0.374 9 | 0.124 9 | 0.281 2 | 0.171 3 |
| rs145010051 | 0.530 0 | 0.470 0 | 0.628 1 | 0.490 0 | 0.499 4 | 0.374 1 | 0.124 1 | 0.280 7 | 0.430 2 |
| rs66477007 | 0.332 5 | 0.667 5 | 0.595 1 | 0.435 0 | 0.445 0 | 0.345 4 | 0.098 5 | 0.263 2 | 0.203 0 |
| rs142221201 | 0.370 0 | 0.630 0 | 0.574 9 | 0.530 0 | 0.467 4 | 0.357 5 | 0.108 7 | 0.270 5 | 0.058 0 |
| rs67426579 | 0.482 5 | 0.517 5 | 0.631 6 | 0.485 0 | 0.500 6 | 0.374 7 | 0.124 7 | 0.281 1 | 0.158 2 |
| rs145941537 | 0.332 5 | 0.667 5 | 0.602 9 | 0.405 0 | 0.445 0 | 0.345 4 | 0.098 5 | 0.263 2 | 0.038 0 |
| rs67365630 | 0.485 0 | 0.515 0 | 0.608 2 | 0.530 0 | 0.500 8 | 0.374 8 | 0.124 8 | 0.281 1 | 0.072 3 |
| rs3064355 | 0.585 0 | 0.415 0 | 0.635 2 | 0.440 0 | 0.486 8 | 0.367 7 | 0.117 9 | 0.276 7 | 0.004 2 |
| rs60564093 | 0.387 5 | 0.612 5 | 0.615 4 | 0.465 0 | 0.475 9 | 0.362 0 | 0.112 7 | 0.273 2 | 0.018 5 |
(n=200)
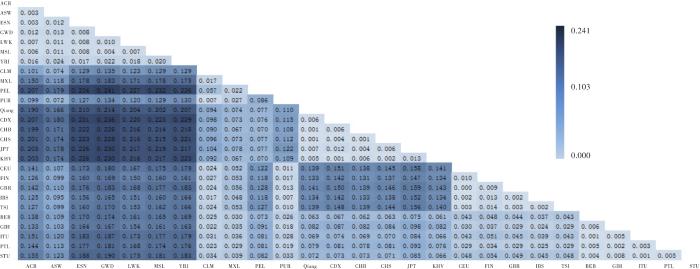
2.5 北川羌族人群与其他人群基于57个A-InDel位点的群体遗传学比较
图1
表4 27个人群的Nei’s遗传距离
Tab. 4
| 人群 | Qiang | CDX | CHB | CHS | JPT | KHV | BEB | GIH | ITU | PTL | STU | ACB | ASW | ESN | GWD | LWK | MSL | YRI | CLM | MXL | PEL | PUR | CEU | FIN | GBR | IBS | TSI |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Qiang | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - |
| CDX | 0.011 | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - |
| CHB | 0.004 | 0.011 | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - |
| CHS | 0.005 | 0.008 | 0.005 | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - |
| JPT | 0.009 | 0.015 | 0.008 | 0.010 | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - |
| KHV | 0.010 | 0.006 | 0.011 | 0.007 | 0.016 | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - |
| BEB | 0.067 | 0.071 | 0.064 | 0.066 | 0.076 | 0.067 | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - |
| GIH | 0.080 | 0.084 | 0.077 | 0.081 | 0.092 | 0.080 | 0.009 | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - |
| ITU | 0.069 | 0.075 | 0.068 | 0.071 | 0.082 | 0.068 | 0.007 | 0.008 | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - |
| PTL | 0.079 | 0.080 | 0.076 | 0.080 | 0.088 | 0.077 | 0.009 | 0.005 | 0.006 | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - |
| STU | 0.070 | 0.072 | 0.070 | 0.070 | 0.081 | 0.066 | 0.009 | 0.009 | 0.005 | 0.008 | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - |
| ACB | 0.177 | 0.179 | 0.174 | 0.176 | 0.179 | 0.175 | 0.097 | 0.091 | 0.113 | 0.103 | 0.114 | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - |
| ASW | 0.161 | 0.164 | 0.158 | 0.161 | 0.166 | 0.158 | 0.082 | 0.074 | 0.095 | 0.086 | 0.095 | 0.005 | - | - | - | - | - | - | - | - | - | - | - | - | - | - | - |
| ESN | 0.191 | 0.194 | 0.189 | 0.191 | 0.195 | 0.190 | 0.117 | 0.109 | 0.135 | 0.124 | 0.136 | 0.003 | 0.008 | - | - | - | - | - | - | - | - | - | - | - | - | - | - |
| GWD | 0.195 | 0.197 | 0.193 | 0.193 | 0.197 | 0.191 | 0.127 | 0.116 | 0.144 | 0.134 | 0.142 | 0.018 | 0.019 | 0.015 | - | - | - | - | - | - | - | - | - | - | - | - | - |
| LWK | 0.185 | 0.184 | 0.184 | 0.185 | 0.188 | 0.182 | 0.111 | 0.102 | 0.126 | 0.118 | 0.125 | 0.005 | 0.007 | 0.005 | 0.017 | - | - | - | - | - | - | - | - | - | - | - | - |
| MSL | 0.186 | 0.189 | 0.186 | 0.187 | 0.192 | 0.183 | 0.116 | 0.110 | 0.133 | 0.125 | 0.132 | 0.005 | 0.008 | 0.005 | 0.014 | 0.005 | - | - | - | - | - | - | - | - | - | - | |
| YRI | 0.194 | 0.195 | 0.191 | 0.193 | 0.193 | 0.192 | 0.115 | 0.108 | 0.133 | 0.124 | 0.134 | 0.003 | 0.008 | 0.003 | 0.015 | 0.004 | 0.005 | - | - | - | - | - | - | - | - | - | - |
| CLM | 0.092 | 0.095 | 0.086 | 0.093 | 0.100 | 0.091 | 0.023 | 0.019 | 0.027 | 0.021 | 0.029 | 0.066 | 0.052 | 0.082 | 0.095 | 0.078 | 0.084 | 0.082 | - | - | - | - | - | - | - | - | - |
| MXL | 0.075 | 0.072 | 0.066 | 0.073 | 0.076 | 0.067 | 0.030 | 0.031 | 0.034 | 0.028 | 0.035 | 0.105 | 0.089 | 0.121 | 0.133 | 0.116 | 0.124 | 0.123 | 0.017 | - | - | - | - | - | - | - | - |
| PEL | 0.072 | 0.070 | 0.065 | 0.073 | 0.070 | 0.066 | 0.068 | 0.078 | 0.071 | 0.069 | 0.071 | 0.159 | 0.144 | 0.175 | 0.184 | 0.170 | 0.177 | 0.178 | 0.047 | 0.021 | - | - | - | - | - | - | - |
| PUR | 0.108 | 0.109 | 0.102 | 0.107 | 0.116 | 0.104 | 0.023 | 0.016 | 0.025 | 0.017 | 0.028 | 0.064 | 0.050 | 0.080 | 0.095 | 0.075 | 0.083 | 0.081 | 0.009 | 0.024 | 0.070 | - | - | - | - | - | - |
| CEU | 0.134 | 0.138 | 0.125 | 0.134 | 0.145 | 0.128 | 0.034 | 0.024 | 0.036 | 0.024 | 0.038 | 0.087 | 0.069 | 0.105 | 0.120 | 0.102 | 0.108 | 0.107 | 0.019 | 0.039 | 0.096 | 0.010 | - | - | - | - | - |
| FIN | 0.131 | 0.134 | 0.121 | 0.130 | 0.137 | 0.127 | 0.038 | 0.029 | 0.040 | 0.026 | 0.042 | 0.084 | 0.069 | 0.103 | 0.120 | 0.098 | 0.105 | 0.102 | 0.022 | 0.042 | 0.095 | 0.014 | 0.010 | - | - | - | - |
| GBR | 0.137 | 0.140 | 0.127 | 0.138 | 0.149 | 0.134 | 0.033 | 0.022 | 0.034 | 0.022 | 0.037 | 0.091 | 0.073 | 0.111 | 0.127 | 0.106 | 0.113 | 0.112 | 0.019 | 0.043 | 0.102 | 0.012 | 0.004 | 0.009 | - | - | - |
| IBS | 0.129 | 0.133 | 0.122 | 0.130 | 0.142 | 0.127 | 0.029 | 0.019 | 0.030 | 0.020 | 0.035 | 0.081 | 0.064 | 0.098 | 0.116 | 0.096 | 0.103 | 0.100 | 0.015 | 0.037 | 0.094 | 0.008 | 0.005 | 0.011 | 0.004 | - | - |
| TSI | 0.136 | 0.138 | 0.128 | 0.135 | 0.146 | 0.131 | 0.033 | 0.022 | 0.034 | 0.022 | 0.037 | 0.083 | 0.068 | 0.103 | 0.119 | 0.100 | 0.105 | 0.103 | 0.020 | 0.042 | 0.101 | 0.010 | 0.005 | 0.012 | 0.006 | 0.005 | - |
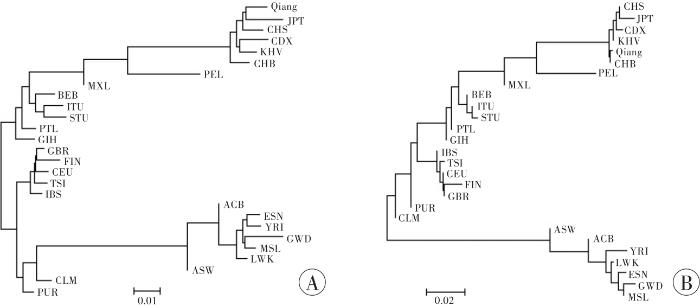
图2
图2
27个人群间的系统发育树
A:基于Nei’s遗传距离;B;基于Fst遗传距离。人群的缩写参表1。
Fig. 2
Phylogenetic trees of 27 populations
3 讨 论
本研究结果显示,经Bonferroni法校正后,57个A-InDel位点均符合Hardy-Weinberg平衡,因此,本研究样本资料可靠。连锁不平衡检验结果显示,57个A-InDel位点在北川羌族人群中不存在连锁不平衡现象(P>0.000 031),提示这些位点是相互独立的遗传标记,可用于法医学鉴定。北川羌族人群57个A-InDel位点中,除rs66595817、rs72085595外,其余55个位点的等位基因频率均在0.3~0.7范围内,表明这57个A-InDel位点在北川羌族人群中的等位基因分布较均衡。由表3可见,Fins、DP、PIC、Ho、He、PEduo、PEtrio的最小值均在rs72085595出现,该位点在已报道的藏族[8]、成都汉族[8]、摩梭人[8]、黑龙江汉族[9]、上海汉族[9]等人群中的Fins、H及PIC也较低,提示该位点在亚洲人群中的遗传多态性可能较低。57个A-InDel位点在北川羌族人群中的CDP值为1-2.974 8×10-24,高于0.999 999 999 999 99,可以应用于法医学个体识别;而CPEtrio值为0.999 999 999,CPEduo值为0.999 062 660(小于0.999 9),提示其可以应用于三联体亲子鉴定,单独应用不能满足二联体亲子鉴定要求,但可作为常规STR检测试剂盒的补充和验证。
Fst反映了特定基因座在群体间分布的差异程度,Fst值越小,说明差异程度越小[10]。有学者[11]认为,Fst值小于0.06可保证所选择的位点适用于不同群体,从而得到稳定的个体识别能力。本研究中rs151335218、rs769299、rs140683187等22个A-InDel位点的Fst值小于0.06,提示该22个A-InDel位点在27个人群间差异很小,可适用于不同群体。另外,rs34421865、rs3076465、rs34287950等35个A-InDel位点的Fst值大于0.06,说明这35个位点在27个人群间基因频率差异较大,在群体遗传学和种群识别方面有重要的应用价值[10]。
遗传距离是用于评估群体间遗传差异或遗传分化的重要参数。本研究中北川羌族人群与北京汉族和南方汉族人群遗传距离最近,与非洲人群遗传距离较远,其中与冈比亚西部人群遗传距离最远,提示遗传距离和实际地域的物理距离区分度基本相似。此外,基于Nei’s遗传距离构建的系统发育树(图2A)显示有4个主要分支(东亚分支、南亚分支、欧洲分支和非洲分支),提示群体所处地理位置与遗传距离密切相关;美洲人群分散在东亚和非洲的分支,可能是因为二战前亚洲及非洲人口迁移至美洲所致[12]。就研究人群而言,北川羌族人群属于东亚分支,与南方汉族和日本人群首先聚类,该结果与王敬方等[6]对四川羌族SNP多态性进行分析得到的结论类似。为了进一步验证27个人群之间的遗传结构,本研究使用基因型数据计算Fst遗传距离并构建了系统发育树(图2B)。基于Fst遗传距离构建的系统发育树群体分布格局与基于Nei’s遗传距离构建的系统发育树相似,但北川羌族与北京汉族人群的遗传关系更为密切。由此可以看出,基于基因频率的Nei’s遗传距离的分析结果与基于基因型的Fst遗传距离的分析结果基本一致,提示这57个A-InDel位点在一定程度上可以用于生物地理祖先推断。
本研究获得了57个A-InDel位点在四川省北川羌族人群中的等位基因频率及遗传学参数,为法医学应用研究提供了基础数据。
续表3
| 位点 | Fdel | Fins | DP | Ho | He | PIC | PEduo | PEtrio | Fst |
|---|---|---|---|---|---|---|---|---|---|
| rs34076006 | 0.462 5 | 0.537 5 | 0.633 8 | 0.475 0 | 0.498 4 | 0.373 6 | 0.123 6 | 0.280 4 | 0.187 7 |
| rs3834231 | 0.345 0 | 0.655 0 | 0.594 6 | 0.460 0 | 0.453 1 | 0.349 8 | 0.102 1 | 0.265 9 | 0.007 0 |
| rs61490765 | 0.392 5 | 0.607 5 | 0.617 6 | 0.465 0 | 0.478 1 | 0.363 2 | 0.113 7 | 0.274 0 | 0.019 9 |
| rs72085595 | 0.760 0 | 0.240 0 | 0.529 5 | 0.370 0 | 0.365 7 | 0.298 3 | 0.066 5 | 0.234 9 | 0.272 1 |
| rs76158822 | 0.477 5 | 0.522 5 | 0.631 2 | 0.485 0 | 0.500 2 | 0.374 5 | 0.124 5 | 0.280 9 | 0.228 6 |
| rs67487831 | 0.385 0 | 0.615 0 | 0.603 4 | 0.490 0 | 0.474 7 | 0.361 4 | 0.112 1 | 0.272 9 | 0.071 7 |
| rs66595817 | 0.272 5 | 0.727 5 | 0.550 6 | 0.425 0 | 0.397 5 | 0.317 9 | 0.078 6 | 0.246 7 | 0.101 5 |
| rs35065898 | 0.495 0 | 0.505 0 | 0.638 6 | 0.470 0 | 0.501 2 | 0.375 0 | 0.125 0 | 0.281 2 | 0.054 1 |
| rs34529638 | 0.370 0 | 0.630 0 | 0.612 5 | 0.450 0 | 0.467 4 | 0.357 5 | 0.108 7 | 0.270 5 | 0.029 5 |
| rs67264216 | 0.607 5 | 0.392 5 | 0.613 5 | 0.475 0 | 0.478 1 | 0.363 2 | 0.113 7 | 0.274 0 | 0.023 3 |
| rs3067397 | 0.647 5 | 0.352 5 | 0.610 6 | 0.425 0 | 0.457 6 | 0.352 3 | 0.104 2 | 0.267 4 | 0.187 7 |
| rs11277697 | 0.617 5 | 0.382 5 | 0.594 9 | 0.505 0 | 0.473 6 | 0.360 8 | 0.111 6 | 0.272 5 | 0.039 7 |
| rs72031009 | 0.465 0 | 0.535 0 | 0.643 8 | 0.450 0 | 0.498 8 | 0.373 8 | 0.123 8 | 0.280 5 | 0.263 8 |
| rs33971783 | 0.577 5 | 0.422 5 | 0.650 7 | 0.385 0 | 0.489 2 | 0.368 9 | 0.119 1 | 0.277 5 | 0.009 6 |
| rs146875868 | 0.485 0 | 0.515 0 | 0.595 8 | 0.550 0 | 0.500 8 | 0.374 8 | 0.124 8 | 0.281 1 | 0.214 2 |
| rs34419736 | 0.630 0 | 0.370 0 | 0.600 6 | 0.480 0 | 0.467 4 | 0.357 5 | 0.108 7 | 0.270 5 | 0.104 6 |
| rs77635204 | 0.545 0 | 0.455 0 | 0.615 8 | 0.510 0 | 0.497 2 | 0.373 0 | 0.123 0 | 0.280 0 | 0.231 3 |
| rs561160795 | 0.517 5 | 0.482 5 | 0.658 4 | 0.405 0 | 0.500 6 | 0.374 7 | 0.124 7 | 0.281 1 | 0.164 6 |
参考文献
InDel遗传标记在法医学领域的研究进展
[J].
Research progress on InDel genetic marker in forensic science
[J].
InDel标记的研究和应用进展
[J].
Progress in research and application of InDel markers
[J].
近十年来羌族族源研究综述
[J].
4
.
A research review of the Qiang’s ethnic origin in the recent ten years
[J].
Analysis of the features of the vernacular plank houses of the Qiang ethnic group in southern Songpan county: A case study of Xiao-xinggou
[J].
贵州9个世居少数民族mtDNA遗传多态性研究
[D].
Study on mtDNA genetic polymorphism of 9 native minorities in Guizhou
[D].
基于27-plex SNPs的四川地区四个族群遗传推断研究
[J].
Gene-tic inference study of four populations in Sichuan province by 27-plex SNPs
[J].
中国北川羌族群体15个STR基因座遗传多态性
[J].
Genetic polymorphism of 15 STR loci in Beichuan Qiang population, China
[J].
Revisiting the genetic background and phylogenetic structure of five Sino-Tibetan-speaking populations: Insights from autosomal InDels
[J].
Forensic features and genetic background exploration of a new 47-autosomal InDel panel in five representative Han populations residing in Northern China
[J].
江苏汉族人群30个插入/缺失位点的遗传多态性
[J].
Genetic polymorphism of 30 InDel loci in Han population from Jiangsu Province
[J].
Isolation and characterization of high-molecular mass DNA from hair shafts
[J].